DNA自组装形成的复杂纳米结构和装置作为合成生物学元件,能够在生命科学、化学、材料学等领域中提供微纳米技术解决方案。在DNA纳米技术领域中,有许多方法能够实现DNA纳米结构的动态变构,包括调节环境因素实现不同DNA结构状态的转换、利用酶对DNA分子的作用实现结构变换,以及经典的黏性末端链置换方法等等。许多的DNA动态系统和装置被成功构建。
近日,清华大学生命学院魏迪明副教授课题组在研究中提出用一种更简便、有效的基于非黏性末端链置换方法的系统,实现DNA纳米结构的动态转换。在该系统中,封闭链(blockers)能够通过竞争置换将已经形成互补配对的DNA链分离,进而实现简单的DNA结构和复杂的二维、三维DNA纳米结构的变换。通过调节封闭链和被竞争结构的浓度比,可有效地实现DNA结构状态的可逆转换。基于概率模型和反应平衡模型,计算机模拟揭示了该体系与传统方法相比的区别和优势。可逆的动态变构反应和简便的反应方向控制是本方法的显著特点。
为了进一步应用在复杂的DNA结构中,研究采用了二维长方形DNA纳米结构和三维长方体DNA纳米结构用于结构变换。在二维体系中,随着结构之间的反应位点从单一位点到多位点发展,结构之间的相互作用呈现协同效应,非黏性末端链置换方法仍然可以发挥转换结构的作用。在三维体系中,非黏性末端链置换不仅体现出其对于结构变换的控制性能,还可以用于构建布尔函数(Boolean functions)。本研究中利用两个单元和四个单元的三维长方体DNA纳米结构分别构建出了4比特输入/2比特输出和16比特输入/8比特输出的多入多出布尔函数(MIMO Boolean functions)。如图1所示,通过封闭链的控制,四种基本三维长方体DNA纳米结构可以形成七种不同的俄罗斯方块。
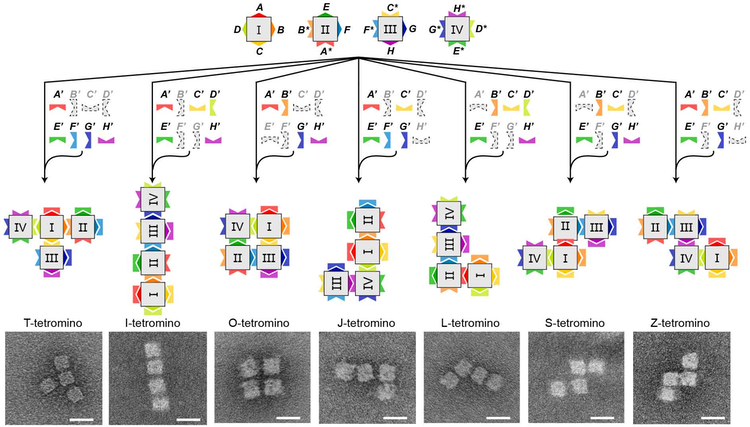
图1基于非黏性末端链置换方法的三维DNA长方体纳米结构单元形成不同的四聚体复合体的操作和结果。四种三维长方体DNA纳米结构单元的四个侧面分别相互配对(相互匹配的颜色的凹凸面代表可以配对的侧面和可配对的封闭链)。当特定的封闭链集合(用彩色表示使用的封闭链,用灰色表示未采用的封闭链)加入到相同的四种单元混合体系中,能够控制形成七种俄罗斯方块中的一种。最下排为电子显微镜成像结果,比例尺:25纳米。
在计算过程中,由于三维DNA长方体纳米结构的外形易于识别,可以用于表示特定系统的状态,因而本研究中将结构的形状信息作为布尔函数运算的输出。进行多入多出布尔函数计算时,可以通过函数之间的组合和迭代,通过不同反应方式得到相同的结果,即用不同的运算过程得到相同的输出,见图2。能够实现在DNA计算过程中观测中间结果,同时也为DNA计算提供了一种条件控制的方法。
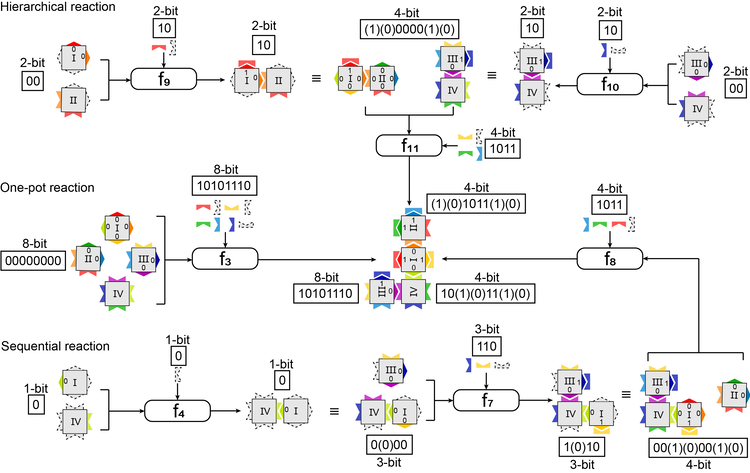
图2基于非黏性末端链置换方法控制信息计算过程。采用三种不同方式反应可以得到相同的J型四聚体俄罗斯方块。第一种是层级式反应(顶部)。两两单元之间形成二聚体,然后再形成四聚体,即两个2比特输入/2比特输出的布尔函数通过组合得到一个4比特输入/2比特输出的函数。第二中是一步法反应(中间),操作与图1所示相同,是一个16比特输入/8比特函数输出的布尔函数。第三种是顺序反应(底部),单元之间依次连接形成四聚体,是三个2比特输入/2比特输出布尔函数之间的迭代。
该研究成果的论文以“非黏性末端链置换方法在DNA动态和计算中的研究”(DNA dynamics and computation based on toehold-free strand displacement)为题于2021年8月17日发表于《自然·通讯》(Nature Communications)期刊上。
多学科深度交叉是此研究的一个鲜明特点,清华大学生命科学学院博士生康宏为本文的第一作者,生命科学学院魏迪明副教授、清华大学自动化系贾庆山教授、香港科技大学的雷克威尔德(Lakerveld)副教授为共同通讯作者。该研究得到国家自然科学基金委、科技部、教育部、清华-北大生命科学联合中心、清华大学结构生物学高精尖中心等基金资助。
① 凡本站注明“稿件来源:中国教育在线”的所有文字、图片和音视频稿件,版权均属本网所有,任何媒体、网站或个人未经本网协议授权不得转载、链接、转贴或以其他方式复制发表。已经本站协议授权的媒体、网站,在下载使用时必须注明“稿件来源:中国教育在线”,违者本站将依法追究责任。
② 本站注明稿件来源为其他媒体的文/图等稿件均为转载稿,本站转载出于非商业性的教育和科研之目的,并不意味着赞同其观点或证实其内容的真实性。如转载稿涉及版权等问题,请作者在两周内速来电或来函联系。





 中国教育在线
中国教育在线



